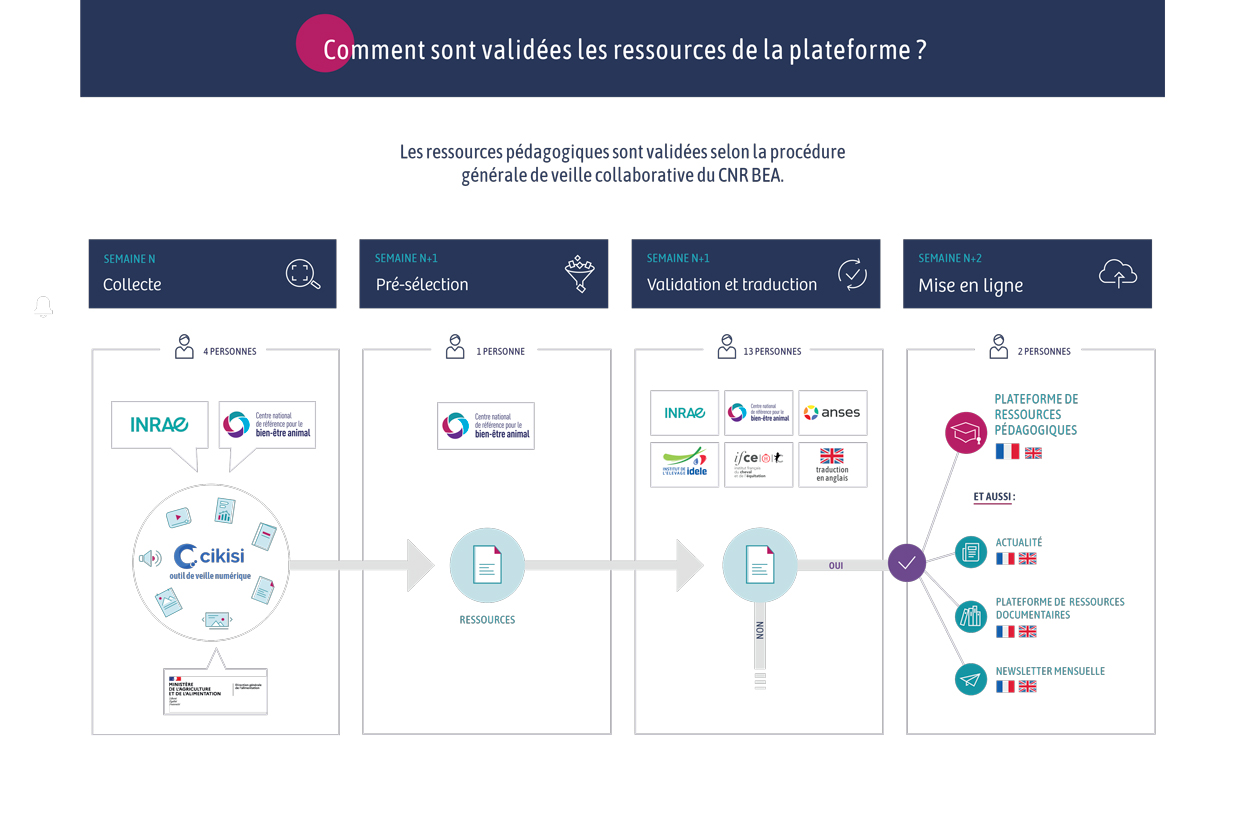
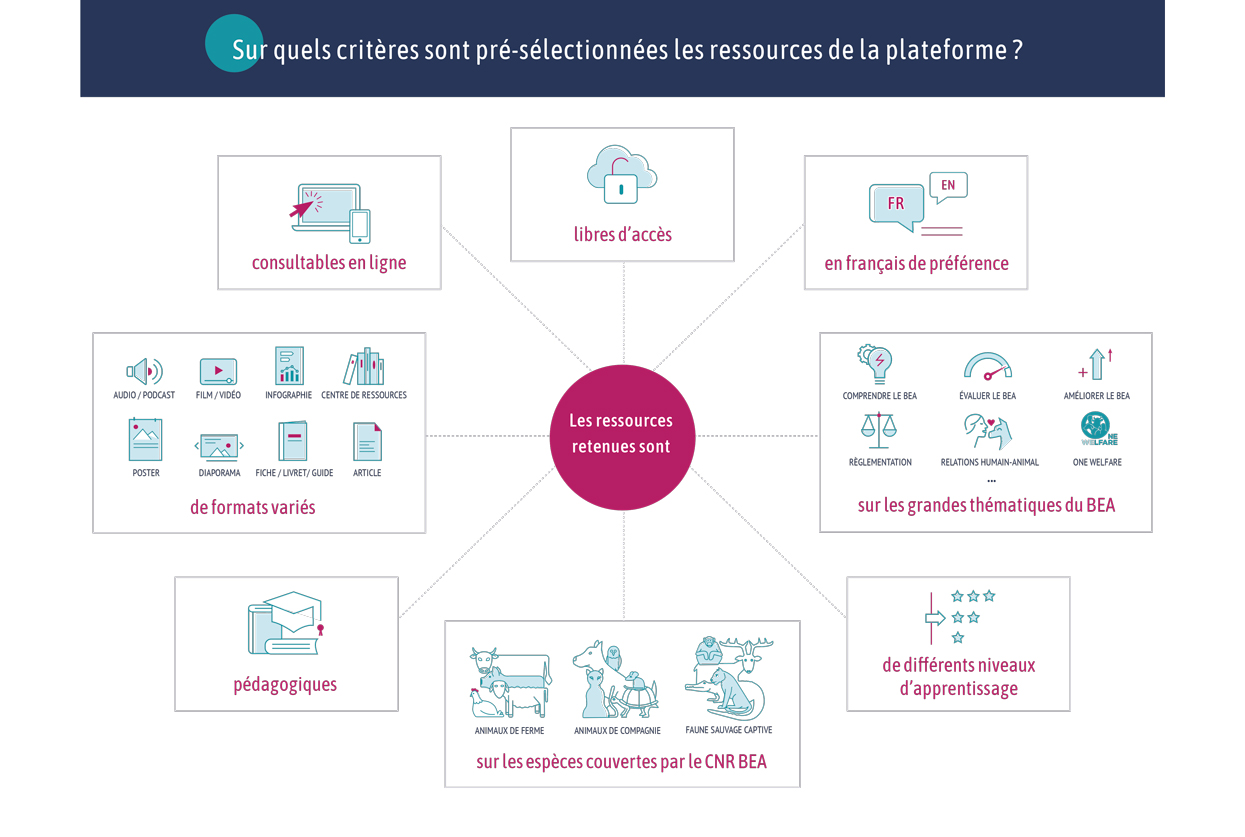
Type de document : article scientifique publié dans Frontiers in Genetics
Auteurs : Aniek Bouwman, Anatolii Savchuk, Abouzar Abbaspourghomi, Bram Visser
Résumé en français (traduction) : La locomotion est une caractéristique importante du bien-être et de la santé dans la production de dinde. Les performances actuelles de l’élevage en matière de locomotion sont souvent basées sur une notation subjective. Des technologies de capteurs pourraient être appliquées pour obtenir une évaluation objective de la démarche des dindes. Les systèmes de mesure inertielle (SMI) mesurent l’accélération et la vitesse de rotation, ce qui en fait des dispositifs intéressants pour l’analyse de la démarche. L’objectif de cette étude était de comparer trois méthodes différentes de détection des pas à partir des données des SMI des dindes. Il s’agit d’une étape essentielle pour l’extraction de caractéristiques futures pour l’évaluation de la locomotion des dindes. Les données provenant de dindes marchant dans un couloir avec des SMI attachés à chaque cuisse ont été annotées manuellement. Nous avons évalué la détection des points de changement, l’approche des extrêmes locaux et la méthode d’amplification des gradients en termes de détection des pas et de précision du point de départ et d’arrivée des pas. Les trois méthodes ont réussi à détecter les pas, mais l’approche par les extrêmes locaux a montré plus de fausses détections. En termes de précision des points de départ et d’arrivée des étapes, la détection du point de changement a donné de mauvais résultats en raison d’un décalage irrégulier important, alors que la méthode d’amplification des gradients était la plus précise. Pour la distance autorisée par rapport aux pas annotés de 0,2 s, la précision de la méthode d’amplification des gradients était de 0,81 et le rappel était de 0,84, ce qui est bien mieux que les deux autres méthodes (<0,61). À une distance autorisée de 1 s, les performances des trois modèles étaient similaires. La méthode d’amplification des gradients a été identifiée comme la plus précise pour la segmentation du signal, avec pour objectif final d’extraire des informations sur la démarche des dindes ; cependant, elle nécessite un ensemble de données d’entraînement annotées.
Résumé en anglais (original) : Locomotion is an important welfare and health trait in turkey production. Current breeding values for locomotion are often based on subjective scoring. Sensor technologies could be applied to obtain objective evaluation of turkey gait. Inertial measurement units (IMUs) measure acceleration and rotational velocity, which makes them attractive devices for gait analysis. The aim of this study was to compare three different methods for step detection from IMU data from turkeys. This is an essential step for future feature extraction for the evaluation of turkey locomotion. Data from turkeys walking through a corridor with IMUs attached to each upper leg were annotated manually. We evaluated change point detection, local extrema approach, and gradient boosting machine in terms of step detection and precision of start and end point of the steps. All three methods were successful in step detection, but local extrema approach showed more false detections. In terms of precision of start and end point of steps, change point detection performed poorly due to significant irregular delay, while gradient boosting machine was most precise. For the allowed distance to the annotated steps of 0.2 s, the precision of gradient boosting machine was 0.81 and the recall was 0.84, which is much better in comparison to the other two methods (<0.61). At an allowed distance of 1 s, performance of the three models was similar. Gradient boosting machine was identified as the most accurate for signal segmentation with a final goal to extract information about turkey gait; however, it requires an annotated training dataset.